推荐产品
公司新闻/正文
应用分享 5—Nature paper:用于靶向治疗的大规模平行蛋白质从头设计
人阅读 发布时间:2018-10-11 18:42

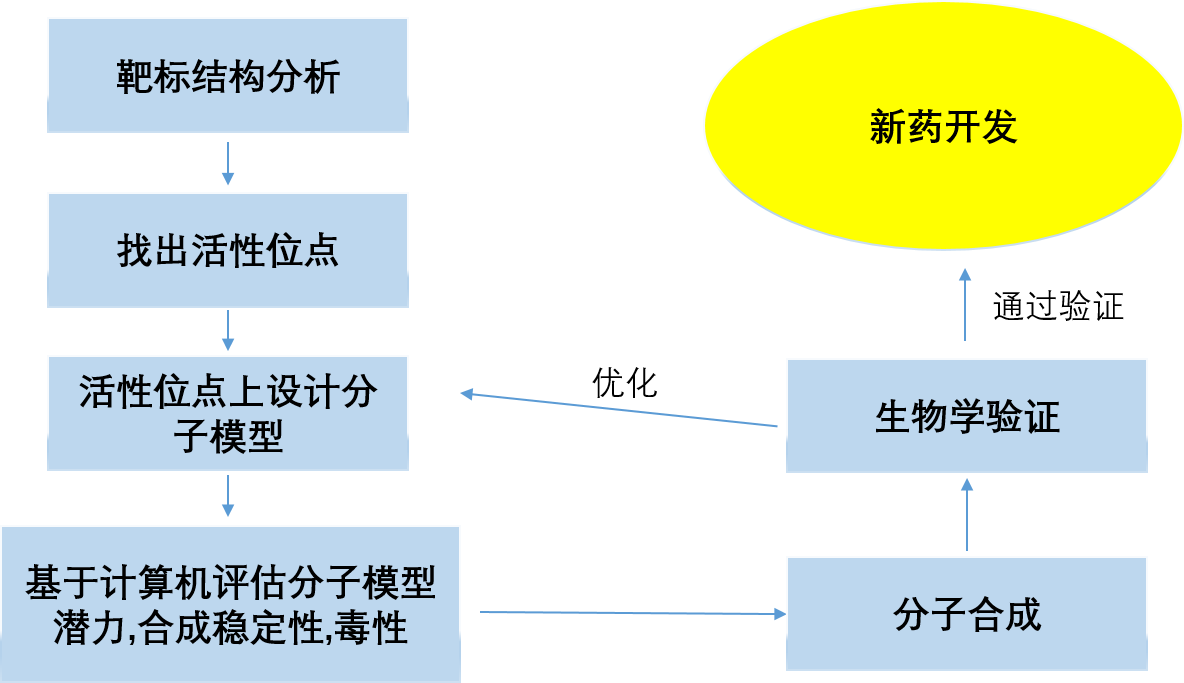
从头药物设计是基于结构生物学的一种设计思路。依赖于对靶标三维结构的深入理解以及化合物合成的全面掌握。从头药物设计提供了一种强有力的工具,使用这种工具,药化学家可以先在计算机上进行药物设计,模拟和验证。然后进行化学合成,生物学验证以及结构解析,从而高效的实现新药发现。
从头药物设计一般流程:
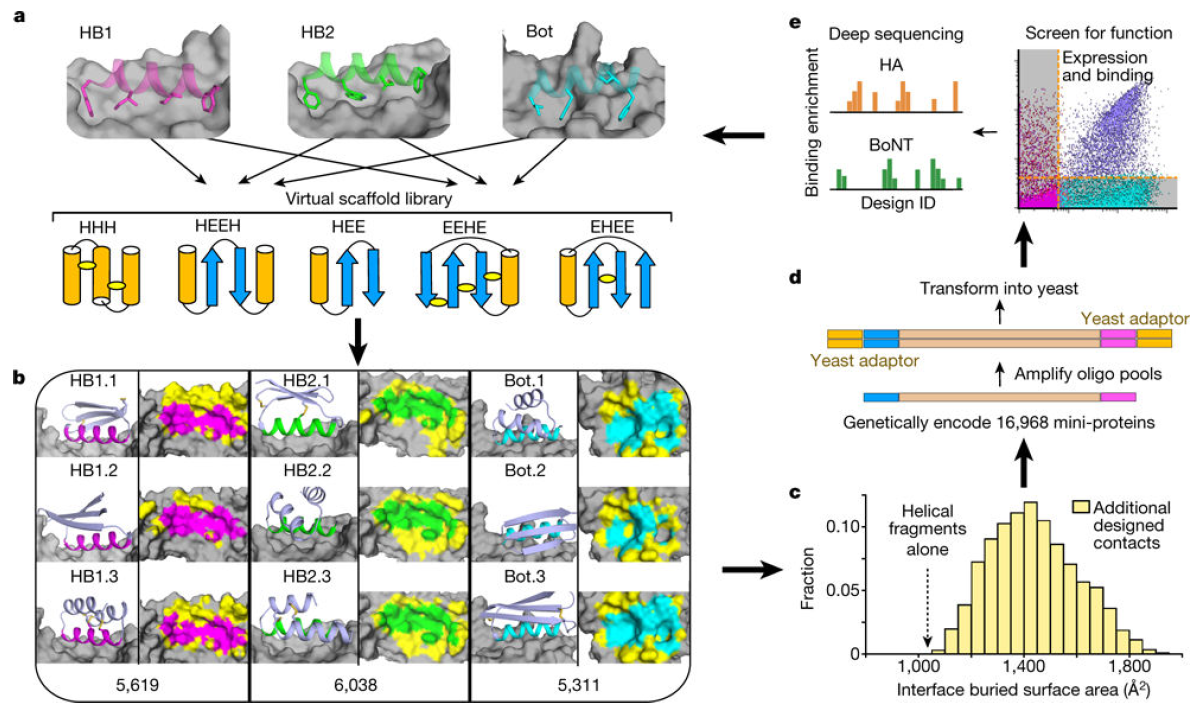
近期 Nature 的一篇文章中提出了整合计算机设计,核苷酸合成,酵母表面展示和二代测序的大规模平行设计方法。这种方法相比较之前的研究能够更大规模对设计结合的蛋白的分析和筛选。为同时检测成千上万种结合和折叠测试提供可能。
大规模平行设计流程:
a. 本文选择甲型 H1N1 流感病毒血凝素和肉毒神经毒素作为靶标,根据各自靶标三维结构,通过计算机分析获得超过 4000 种几何骨架,其中包含了五种拓扑学结构(HHH,HEEH,HEE,EEHE,EHEE)。
b. 采用 Rosetta 组合序列优化设计了各种各样与靶标结合的小分子肽。
c. 该设计大大提高了界面包埋表面面积。
d. 合成所有设计小分子肽对应的寡核苷酸并共转化到酵母展示载体中,产生了用于展示 16968 个蛋白的酵母库。
e. 通过流式细胞分选技术,将设计结合靶标的展示酵母细胞分选出来,进一步用于细胞深度测序。
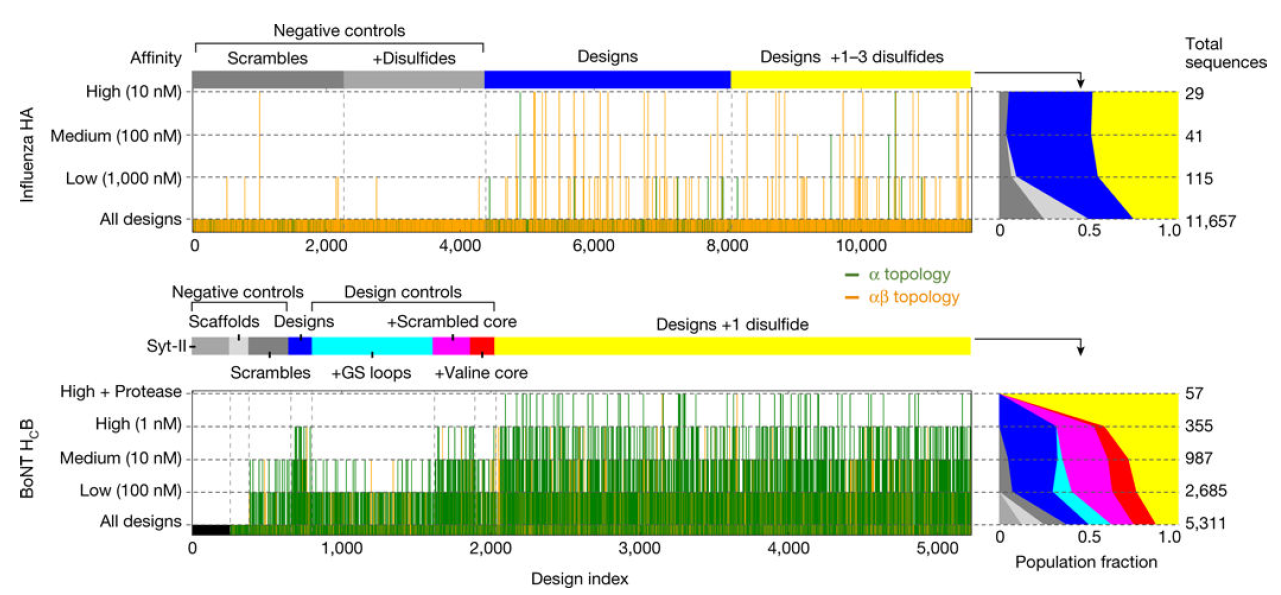
大规模平行验证流程:
通过深度测序酵母库,几乎全部显示了全长基因,HA库显示了 11657 个序列中的 11002 个(94.4%),BoNT 库显示了 5311 个序列中的 5306 个(99.9%)。结果显示在提高严格性(降低靶标浓度)的情况下,流式细胞分选酵母库能够大大减少不同序列的数量。
分子合成:
将设计的基因整合到 Pet-28(+) E.coli 质粒表达,进一步通过亲和层析和分子筛层析纯化得到蛋白。应用质谱技术验证蛋白特性。或者直接通过已知肽序列合成小分子肽。然后应用圆二色谱,分子互作验证蛋白结构及分子间相互作用。
生物学验证:
通过流感中和试验与肉毒神经毒素中和试验;小鼠体内使用设计的小分子肽治疗流感,应用 ELISA 检测小鼠体内免疫状态。
结果:
本文设计出针对流感血凝素(Influenza HA),肉毒杆菌神经毒素(BoNT)的 2618 个高亲和性结合蛋白中部分设计产物表现出极强的稳定性,且不会引发免疫反应,即使多次给药依然能够针对流感病毒起到防御和治疗保护作用。大规模平行设计方法为今后临床治疗和诊断应用提供了希望。
本文大规模筛选关键依赖于酵母表面展示技术的应用。然而,什么是酵母表面展示?
简单来说就是使表达的多肽以融合蛋白形式展现在细胞表面,保持相对独立空间结构和生物活性。
酵母表面展示分选方法:
本文在前期计算机系统设计优化的核苷酸整合到载体上并在酵母中表达,其中每个载体都标记有亲和素或者 C-Myc。然后在使用抗亲和素或者 C-Myc 抗体与酵母结合。最后结合带有荧光标记(FITC)的二抗。标记有荧光的酵母表面通过流式细胞分选系统分选出来,进一步通过深度测序验证分析(见下图)。

本文酵母表面展示筛选的所有工作都在索尼SH800S流式细胞分选仪上完成,该设备具有全自动开机校准,在快速分选下能够保持高准确性和活性,为本文大规模平行筛选打下夯实基础。
参考文献:Aaron Chevalier1,2,*, Daniel-Adriano Silva1,2,*, Gabriel J. Rocklin1,2,*, Derrick R. Hicks1,2,3, Renan Vergara1,2,4, Patience Murapa5, Steffen M. Bernard6,7, Lu Zhang8,9, Kwok-Ho Lam10, Guorui Yao10, Christopher D. Bahl1,2, Shin-Ichiro Miyashita11,12, Inna Goreshnik1, James T. Fuller5, Merika T. Koday5,13, Cody M. Jenkins5, Tom Colvin1, Lauren Carter1,2, Alan Bohn5, Cassie M. Bryan1,2, D. Alejandro Fernández-Velasco4, Lance Stewart2, Min Dong11,12, Xuhui Huang9, Rongsheng Jin10, Ian A. Wilson6,7, Deborah H. Fuller5, and David Baker1,. “Massively parallel de novo protein design for targeted therapeutics.” Nature. 2017 October 05; 550(7674): 74–79. doi:10.1038/nature23912.
愿我们的努力为您的实验增添一份助力!
获取更多资讯,请发消息给索尼生命科学公众号,或通过邮件联系我们
电话:15201632245
Email: shuo.xiao@sony.com










